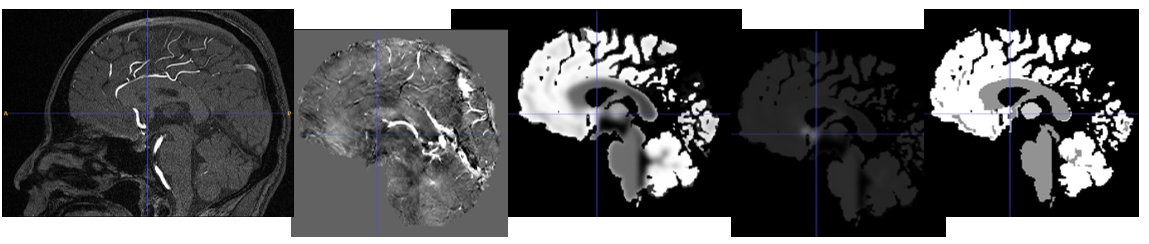
Celem projektu jest zbadanie wpływu podstawowych zjawisk wykorzystywanych w urządzeniach rezonansu magnetycznego (MRA) na dokładność modelowania i parametryzacji układu naczyń krwionośnych mózgu.
Planuje się udowodnienie dwóch hipotez. Ponieważ rozdzielczość przestrzenna obrazów RM dla ustalonego natężenia pola magnetycznego jest ograniczona, to modele geometryczne naczyń mogą być budowane tylko dla gałęzi o dużej średnicy (w stosunku do długości boku woksela obrazu). Wiadomo też, że naczynia cieńsze stanowią ciągłe przedłużenie naczyń grubych, a obszary nimi wypełnione mogą być ilościowo charakteryzowane za pomocą parametrów statystycznych tekstury lub zmierzonych techniką SWI map gęstości naczyń. Obserwacje te pozwalają na sformułowanie hipotezy, że dołączenie syntezowanych numerycznie drzew cienkich naczyń (o parametrach statystycznych dopasowanych do obrazów) do rozgałęzień modelu geometrycznego naczyń o dużej średnicy pozwoli na ciągłe modelowanie właściwości drzewa naczyń w znacznie szerszej skali średnic niż to jest obecnie możliwe. Druga hipoteza mówi, że połączenie różnych metod segmentacji obrazów 3D (m.in. metody poziomicowej z morfologią matematyczną i regularyzacją stosownych równań) pozwoli budować modele odporne na artefakty (m.in. skoki kontrastu) towarzyszące sekwencjom służącym do obrazowania tętnic i żył.
Kierownik i wykonawcy: prof. A. Materka – kierownik,
prof. J. R. Reichenbach, dr A. Deistung, dr hab. M. H. Strzelecki, dr hab. P. M. Szczypiński, dr hab. A. J. Majos, dr inż. M. Kociński, dr inż. A. J. Klepaczko, mgr A. Chmielewska-Pawlicka.
Lata: 2013 – 2016
Rodzaj projektu: NCN-MN, NCN HARMONIA; badania podstawowe
Najważniejsze publikacje, które powstały w wyniku realizacji projektu:
- A. Klepaczko, P. Szczypiński, G. Dwojakowski, M. Strzelecki, A. Materka, Computer Simulation of Magnetic Resonance Angiography Imaging: Model Description and Validation, PLoS One 2014;9(4):e93689, DOI: 10.1371/journal.pone.0093689 (IF=3,534).
- A. Klepaczko, A. Materka, P. Szczypiński, M. Strzelecki, Numerical Modeling of MR Angiography for Quantitative Validation of Image-Driven Assessment of Carotid Stenosis, IEEE Transactions on Nuclear Science, 2015;62(3):619-627, DOI: 10.1109/TNS.2015.2433925 (IF=1,283).
- M. Kociński, J. Blumenfeld, A. Materka, A. Deistung, B. Serres, JR. Reichenbach (2015) Automated centerline-based modeling of tubular blood vessel segments from 3D MRA. Magnetic Resonance Materials in Physics, Biology and Medicine MAGMA, Vol 28, Suppl 1, Oct 2015, 32nd Annual Scientific Meeting, Edinburgh, October 1-3 2015, pp. S381-S382, DOI: 10.1007/s10334-015-0489-0, © Springer.
- J. Blumenfeld, M. Kociński, A. Materka (2015) A centerline-based algorithm for estimation of blood vessels radii from 3D raster images. IEEE SPA 2015 (Int. Conf on Signal Processing, Algorithms, Arrangements and Applications), 26-28 Sept 2015, Poznań, pp. 38-43, © IEEE.
- A. Materka, M. Kocinski, J. Blumenfeld, A. Klepaczko, A. Deistung, B. Serres, JR. Reichenbach (2015) Automated Modeling of Tubular Blood Vessels in 3D MR Angiography Images, 9th International Symposium on Image and Signal Processing and Analysis (ISPA 2015) September 7-9, 2015, Zagreb, Croatia, pp. 56-61, © IEEE.

|